Le pneumocoque au centre de trois publications à l'UNIL
L’équipe du Prof. Jan-Willem Veening au Département de microbiologie fondamentale de l’UNIL publie trois études quasi en simultané, respectivement dans les revues « eLife », « PNAS » et « Cell Host & Microbe ». Au cœur de ses recherches : le pneumocoque, un pathogène humain responsable de multiples infections parfois létales.
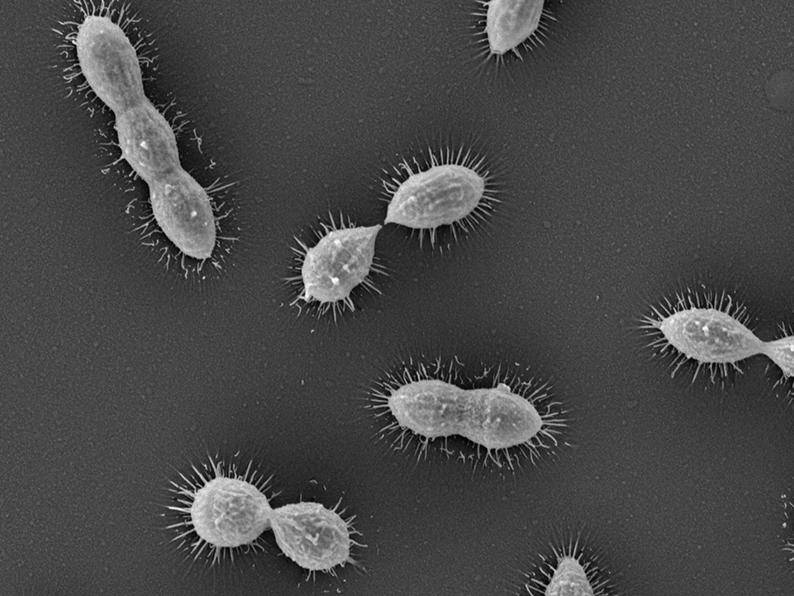
C’est bien trois papiers que le groupe de recherche de Jan-Willem Veening, le « Veening Lab », au Département de microbiologie fondamentale de la Faculté de biologie et de médecine de l’UNIL, a le plaisir de voir paraître dans les périodiques eLife, PNAS et Cell Host & Microbe. Point commun à toutes ces études : le pneumocoque. De son nom latin Streptococcus pneumoniae, cette bactérie est propre à l’espèce humaine. Présente chez 80% des enfants et 20% des adultes, elle colonise de préférence la région du nasopharynx (partie supérieure du pharynx), généralement sans symptôme. Le microbe peut toutefois se révéler pathogène. Il est responsable d’infections à sévérité variable, telles que la pneumonie ou la méningite, et tue chaque année plus d’un million de personnes à travers le monde. L’usage intensif d’antibiotiques a rendu le germe résistant à la plupart d’entre eux (pénicilline, érythromycine, tétracycline, etc.), ce qui constitue un réel enjeu de santé publique.
eLife
L’étude parue dans le journal scientifique en libre accès s’intéresse plus particulièrement aux mécanismes à l’origine du développement, chez le pneumocoque, de résistances aux antimicrobiens et de stratégies d’évitement des vaccins. Pourquoi et comment cette bactérie devient-elle résistante à un antibiotique? Streptococcus pneumoniae acquiert sa résistance soit en modifiant son propre ADN, soit en intégrant des gènes résistants présents dans l’environnement et provenant d’autres bactéries. Ces dernières peuvent appartenir, ou non, à la même espèce et ne sont pas nécessairement pathogènes. La transformation du matériel génétique du pneumocoque qui engendre l’acquisition de résistance n’est possible que lorsque le microbe active un processus appelé « compétence ». Dans cette étude, réalisée en collaboration avec des chercheurs du Laboratoire de microbiologie et génétique moléculaires de l’Université de Toulouse, il est démontré, par analyse de cellule individuelle, que le pneumocoque peut absorber et intégrer très efficacement l'ADN exogène, quel que soit l'état de son cycle cellulaire.
Découvrir l’article dans eLife
PNAS
Alors que le pneumocoque peut se révéler très néfaste pour notre santé, il cohabite également de manière commensale (sans danger pour l’homme) dans la flore du nasopharynx. Dans ce second papier, les microbiologistes se demandent comment Streptococcus pneumoniae « switche » d’un état commensal à un état pathogène, engendrant de multiples pathologies. Encore mal compris, ce processus implique très certainement des variations dans l’expression des facteurs de virulence. Pour mener à bien leurs investigations, les chercheurs ont utilisé des approches de biologie synthétique. Un réseau de gènes de régulation synthétiques a ainsi été utilisé afin de tester et contrôler les niveaux de virulence in vivo chez la souris infectée par le pneumocoque.
Cell Host & Microbe
Dans cette troisième publication, les biologistes ont étudié le nombre de bactéries qui survivent après une première réponse immunologique de l’hôte et vont rendre ce dernier malade en se répliquant. Pour ce faire, ils ont développé un nouvel outil d’analyse, le CRISPRi-seq. Grâce à cette technique, ils ont pu identifier in vivo chez la souris les gènes bactériens essentiels à l'infection, à l’échelle du génome et en une seule étape de séquençage. En collaboration avec l'Université de Californie de San Diego et l'Institut Pasteur de Lille, ils ont pu montrer que la plupart des pneumocoques meurent avant le déclenchement de la pneumonie chez le rongeur ; au final, seul un petit nombre de microbes restants vont rendre l’animal malade. Les scientifiques ont également identifié, chez cette bactérie, des gènes qui jouent un rôle important lors de surinfection par le virus de la grippe A (H3N2).
par Manuela Palma de Figueiredo - Communication FBM